使用手册(目录号:KINGBIO-1402)
本试剂盒用于快速构建SgRNA体外转录载体,可以通过T7-RNA聚合酶体外转录获得SgRNA。本试剂盒还提供可用于体外转录Cas9酶mRNA的质粒,可用于后续通过显微注射SgRNA与Cas9酶mRNA制备“基因敲除”或“基因敲入”动物。
(1)线性化pHMG-T7-SgRNA质粒;(20ng/µl,20 µl)
(2)线性化pHMG-Cas9质粒;(0.5µg/µl,20 µl)
本试剂盒不提供,但可能需要:
(1)感受态大肠杆菌(如:DH5α)
(2)T4 DNA连接酶及缓冲液
-20℃
目标基因的基因组序列的信息,可从NCBI、Ensembl或UCSC等数据库获取。
http://www.ncbi.nlm.nih.gov/
http://www.ensembl.org/index.html
https://www.genome.ucsc.edu/
根据研究目的,在合适位置寻找并选择CRISPR-Cas9靶点。一般可在目标基因ATG 之后,编码序列的前2/3 区域,且不在最后一个外显子上;若需要,最好能破坏目标蛋白重要的结构域和/或所有的转录本。可以利用网上的CRISPR-Cas9工具网站设计CRISPR-Cas9靶点。
http://crispr.mit.edu/
http://zifit.partners.org/ZiFiT/CSquare9Nuclease.aspx
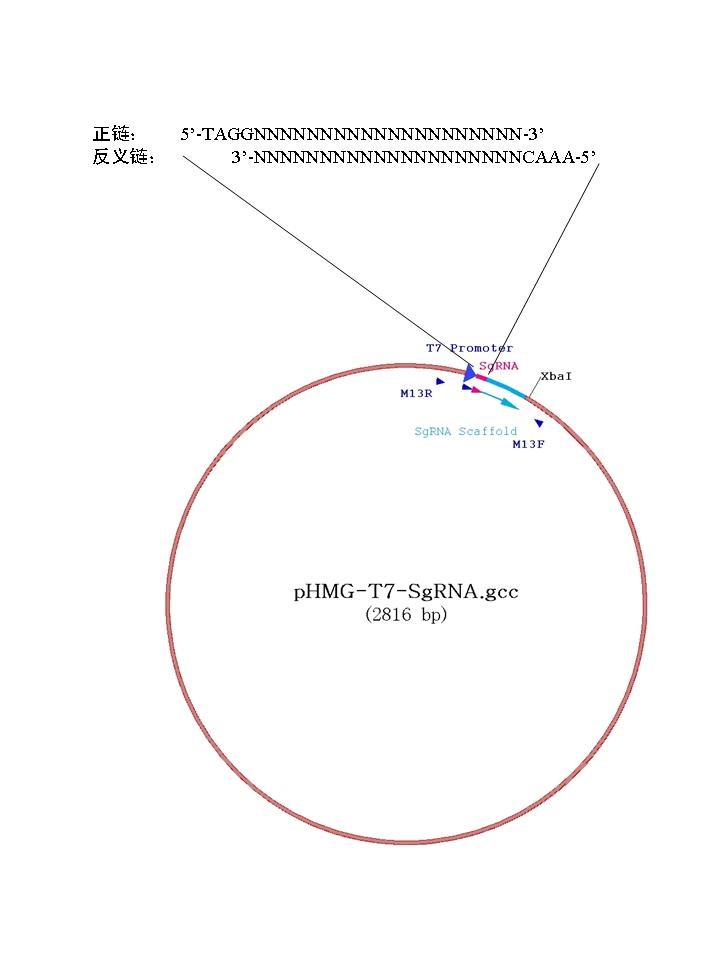
CRISPR-Cas9 靶点识别序列通常含20个碱基,紧邻靶点3’端的3个碱基构成 PAM 区,并遵循NGG的原则,完整靶点序列为 (N)20NGG。Cas9靶点可在cDNA的正义链也可在反义链上。
根据将要进行打靶的位置设计并合成互补的Oligos*:
正链: 5’-TAGGNNNNNNNNNNNNNNNNNNN-3’
反义链: 3’-NNNNNNNNNNNNNNNNNNNCAAA-5’
*注:下划线部分为酶切位点的粘性末端,能够确保发生退火后的Oligos能够定向克隆到载体中。
将上述Oligos按照100µM的浓度各取20µl混合,放置入1.5mL的螺纹口EP管中。取500mL烧杯,加入300mL水,微波炉加热到沸腾。将含有Oligos的EP管,放入浮漂中,然后置于沸水中,自然冷却至室温。退火后的Oligos可以直接用于后续的连接反应,或放置于-20℃保存。
连接反应按照下述比例进行:
实验组:
pHMG-T7-SgRNA 2µl
Oligos 8 µl
T4 DNA 连接酶 2µl
10×连接酶缓冲液 2 µl
H2O 6 µl
20 µl
负对照组:
pHMG-T7-SgRNA 2µl
Oligos 0 µl
T4 DNA 连接酶 2 µl
10×连接酶缓冲液 2 µl
H2O 14 µl
20 µl
16~25 ℃, 1~4小时(或者4℃过夜)。
各取1~2µl上述连接产物,转化感受态大肠杆菌,涂布氨苄青霉素(Ampicillin)平板,37℃培养12-16小时。
比较实验组与对照组平板上的大肠杆菌克隆数,当实验组大肠杆菌克隆数比对照组至少高5~10倍时,挑取6~12个单克隆,置于5mL LB培养基,37℃摇菌过夜。
抽取质粒,用M13R测序引物(5’-AACAGCTATGACCAT-3’),测序鉴定插入片段是否正确。
6.1.1仔细检查感受态大肠杆菌的转化效率;一般情况下,感受态大肠杆菌的转化效率需要达到>1×107。如果转化效率过低,请更换新的感受态大肠杆菌。
6.1.2 仔细检查T4DNA连接酶活性;如果活性过低,更换新的T4DNA连接酶。
6.2.1 连接入SgRNA的pHMG-T7-SgRNA 质粒,需要线性化后,才能够用于后续的体外转录实验。建议用Xba I 对获得的质粒进行线性化。此外,BamH I, Kpn I与EcoR I也可以用于质粒的线性化。需注意的是,在合成的Oligos上不能含上述酶切位点。
6.2.2 用于体外转录Cas9酶的pHMG-Cas9质粒,已经被线性化,可以直接用于后续的体外转录实验。